1. 安装
library(devtools)
devtools::install_github("Moonerss/CIBERSORT")
library(CIBERSORT)
library(ggplot2)
library(dplyr)
library(ggthemes)
library(pheatmap)
library(tibble)
library(tidyr)
library(ggpubr)
library(ggsci)
library(ggthemes)2. 数据准备
需要两个数据:LM22和你需要分析的表达矩阵,我的是bulkRNA的表达矩阵,tpm标准化后的
#读取LM22文件(免疫细胞特征基因文件)
sig_matrix <- system.file("extdata", "LM22.txt", package = "CIBERSORT")
#表达矩阵文件
exp <- read.table(file="tpm_exp.txt",row.names = 1)3. 运行
res <- cibersort(sig_matrix, tpm_exp, perm = 1000, QN = F)
#QN如果是芯片设置为T,如果是测序就设置为F
write.table(res, "res.txt",
sep = "\t", row.names = T, col.names = T, quote = F)4. 可视化
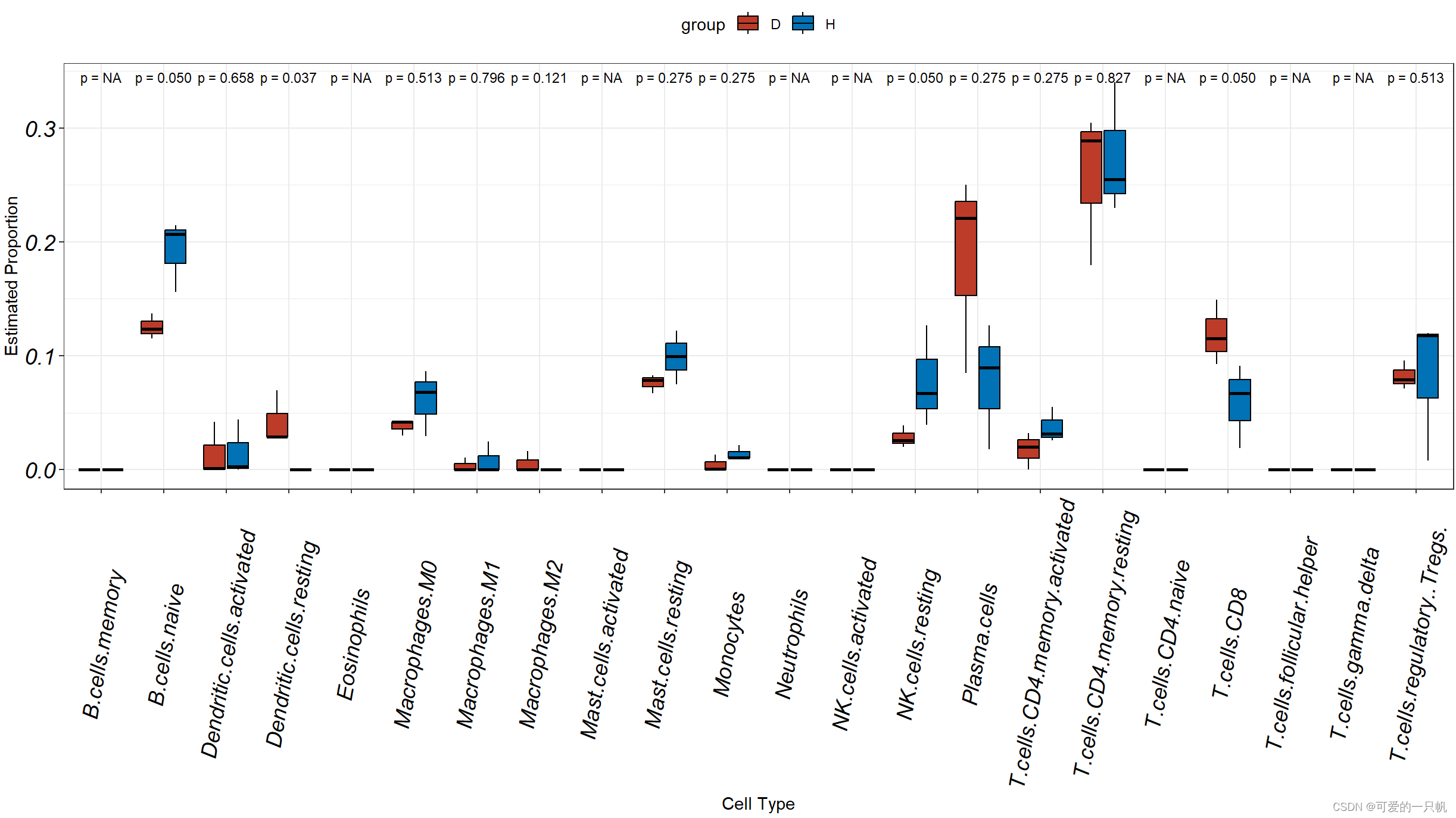
#1.H和D组箱线图
res1 <- data.frame(res[,1:22])%>%
mutate(group = c(rep('H',3),rep('D',3)))%>%
rownames_to_column("sample")%>%
pivot_longer(cols = colnames(.)[2:23],
names_to = "cell.type",
values_to = 'value')
ggplot(res1,aes(cell.type,value,fill = group)) +
geom_boxplot(outlier.shape = 21,color = "black") +
theme_bw() +
labs(x = "Cell Type", y = "Estimated Proportion") +
theme(legend.position = "top") +
theme(axis.text.x = element_text(angle=80,vjust = 0.5,size = 14,face = "italic",colour = 'black'),
axis.text.y = element_text(face = "italic",size = 14,colour = 'black'))+
scale_fill_nejm()+
stat_compare_means(aes(group = group),label = "p.format",size=3,method = "kruskal.test")
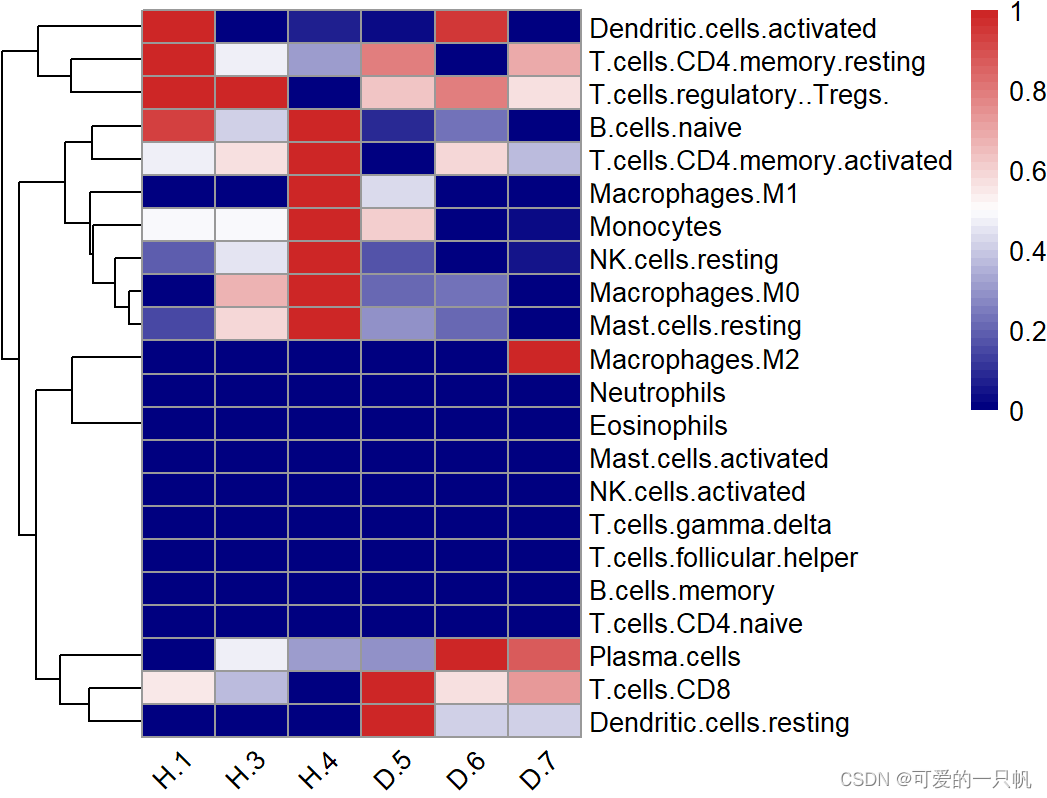
#2.热图
#展示所有的免疫细胞
normalize <- function(x) {
if((max(x) - min(x)) == 0){
return(mean(x))
}else{
return((x - min(x)) / (max(x) - min(x)))
}
}
res1 <- res[,-(23:25)]
res2 <- apply(res1, 2,normalize)
res2 <- t(as.data.frame(res2))
pheatmap(res2,
angle_col = "45",
show_colnames = T,
cluster_cols = F,
color = colorRampPalette(c("navy", "white", "firebrick3"))(50))
#展示在一半以上样本里丰度大于0的免疫细胞
k <- apply(res1,2,function(x) {sum(x == 0) < nrow(exp)/2})
table(k)
#FALSE TRUE
#11 11
res3 <- as.data.frame(t(res1[,k]))
pheatmap(res3,scale = "row",
angle_col = "45",
show_colnames = T,
cluster_cols = F,
color = colorRampPalette(c("navy", "white", "firebrick3"))(50))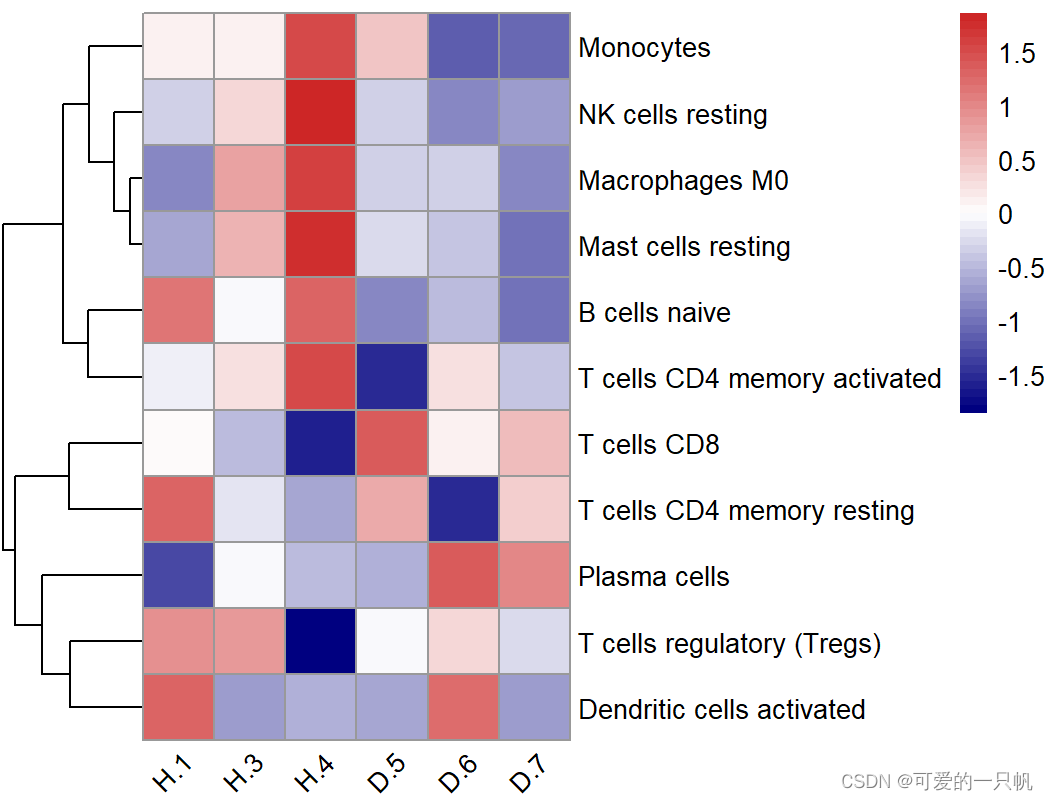
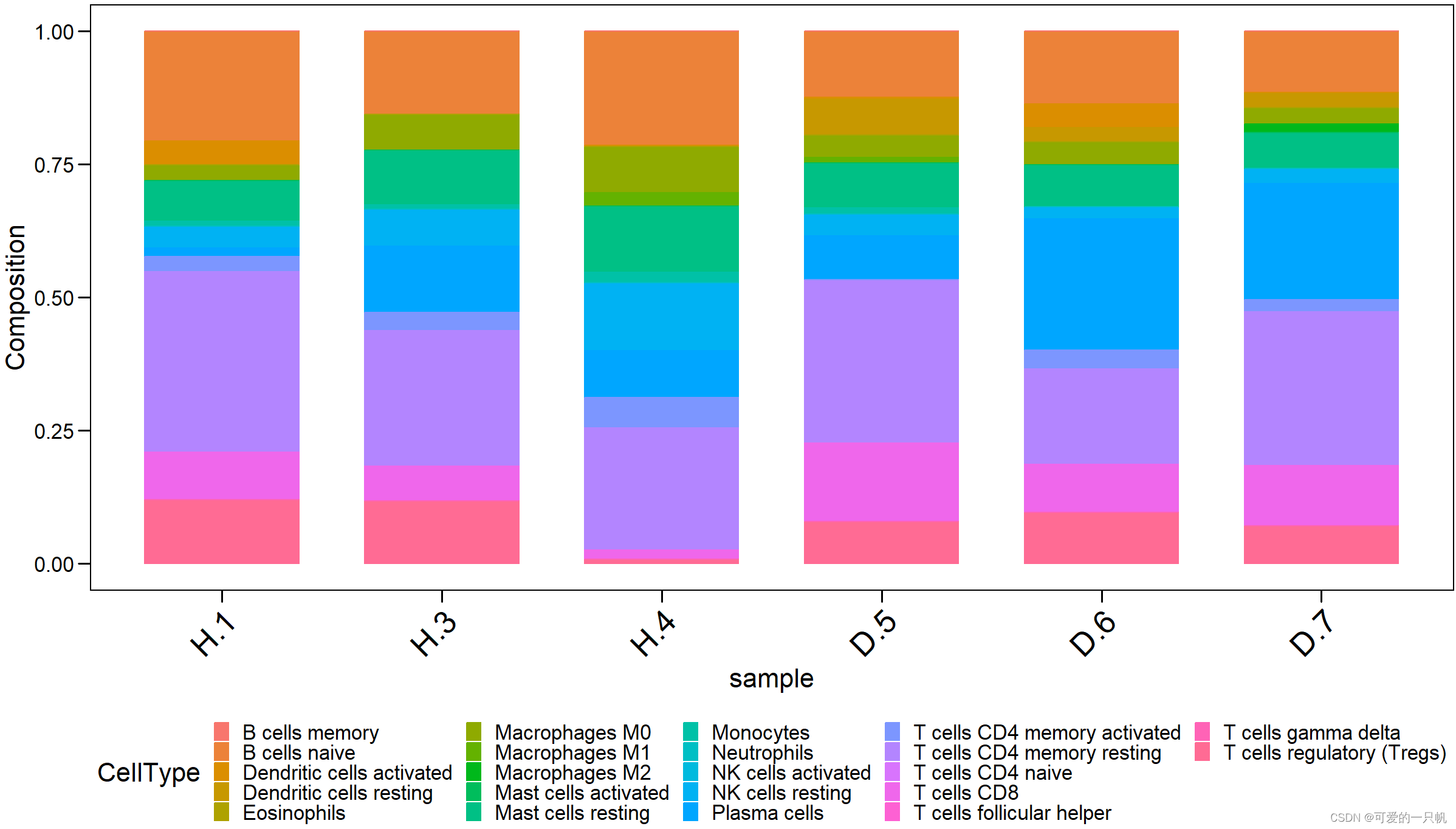
#3.柱状图
res4 <- exp %>%
as.data.frame() %>%
rownames_to_column("sample") %>%
pivot_longer(cols = 2:23,
names_to = "CellType",
values_to = "Composition")
ggbarplot(
res4,
x = "sample",
y = "Composition",
size = 0.5,
fill = "CellType",
color = "CellType") +
theme_base() +
theme(axis.text.x = element_text(
angle = 45,
hjust = 1,
vjust = 1,
size = 20),
legend.position = "bottom",
legend.key.size = unit(10,"pt")
)
参考:量化免疫浸润时CIBERSORT的注意事项。 · Issue #694 · gege-circle/home · GitHub




 该文详细介绍了如何使用R包CIBERSORT进行免疫细胞浸润分析,包括安装CIBERSORT库,准备TPM标准化后的表达矩阵数据,运行CIBERSORT算法以及通过箱线图、热图和柱状图对结果进行可视化。此外,还提供了数据预处理和结果解读的注意事项。
该文详细介绍了如何使用R包CIBERSORT进行免疫细胞浸润分析,包括安装CIBERSORT库,准备TPM标准化后的表达矩阵数据,运行CIBERSORT算法以及通过箱线图、热图和柱状图对结果进行可视化。此外,还提供了数据预处理和结果解读的注意事项。
















 7251
7251










