禁止商业或二改转载,仅供自学使用,侵权必究,如需截取部分内容请后台联系作者!
文章目录
介绍
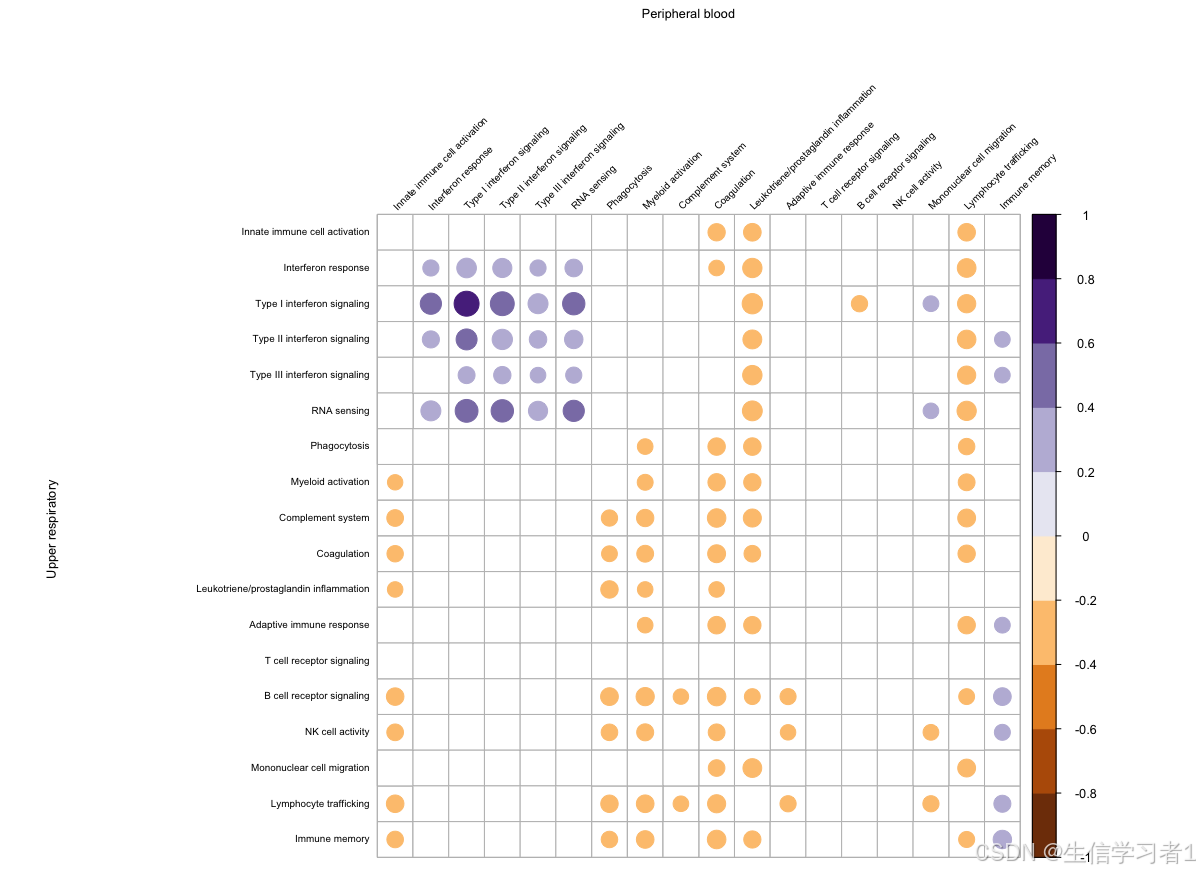
基因集变异分析(Gene Set Variation Analysis,简称GSVA)是一种用于评估样本中基因集活性的计算方法。GSVA的核心原理是将基因表达矩阵中的数据转换为基因集得分,以此来反映特定基因集在单个样本中的活性。这种方法不依赖于差异表达分析,而是通过无监督的方式量化基因集在样本中的富集程度。GSVA使用非参数的方法,如核密度估计,来计算每个基因集的得分,从而避免了对基因集内基因表达分布的假设。这种方法特别适用于探索性分析,可以帮助研究人员识别在不同条件下活跃的生物学通路。
在进行GSVA分析后,我们通常会对不同样本分组间相同通路的活性得分进行比较,以探究它们之间的相关性。这时,我们可以使用斯皮尔曼等级相关系数(Spearman’s rank correlation coefficient)来进行分析。斯皮尔曼相关系数是一种非参数的统计方法,用于评估两个变量之间的相关性。它通过计算变量值的等级(即排序位置)之间的皮尔逊相关系数来评估









 订阅专栏 解锁全文
订阅专栏 解锁全文

















 1029
1029

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










